Arbre phylogénétique

Un arbre phylogénétique est un arbre schématique qui montre les relations de parenté entre des groupes d'êtres vivants. Chacun des nœuds de l'arbre représente l'ancêtre commun de ses descendants ; le nom qu'il porte est celui du clade formé des groupes frères qui lui appartiennent, non celui de l'ancêtre qui reste impossible à déterminer. L'arbre peut être enraciné ou pas, selon qu'on est parvenu à identifier l'ancêtre commun à toutes les feuilles. Charles Darwin fut un des premiers scientifiques à proposer une histoire des espèces représentée sous la forme d'un arbre.
Les arbres phylogénétiques actuels prennent la forme de cladogrammes, schémas minimisant les transformations (principe de parcimonie) de telle façon que les synapomorphies soient significatives de liens phylogénétiques entre organismes, liens conçus sous la forme d'hypothèses testables.
Les arbres phylogénétiques ne considèrent ni les transferts horizontaux ni les hybridations, et un nouveau modèle se développe en phylogénie, celui de graphe ou réseau phylogénétique qui permet de les prendre en compte, ainsi que les recombinaisons.
Historique[modifier | modifier le code]
Charles Darwin pensait que la phylogénie, c'est-à-dire l'étude de l'évolution des organismes vivants en vue d'établir leur parenté, pouvait être représentée sous la forme d'un arbre de vie, ou arbre évolutif. Le concept d'une organisation du monde et de ses habitants remonte à bien plus longtemps. Déjà dans la Scala naturæ ou la « grande chaîne de la vie », le monde est composé d'un grand nombre de liens hiérarchiques, des éléments les plus fondamentaux et basiques tels les minéraux et les végétaux jusqu'à la plus haute perfection, Dieu. Cette conception du monde est largement acceptée par la plupart des savants européens depuis l'époque de Lucrèce jusqu'aux révolutions scientifiques de Copernic (1473-1543) et de Darwin et l'ultime épanouissement de la Renaissance.
Les premiers arbres phylogénétiques[modifier | modifier le code]
L'arbre est utilisé depuis l'Antiquité comme métaphore (par exemple l'arbre de Porphyre) mais jamais dans un sens généalogique. L'image de l'arbre de vie apparaît bien dans le dernier tiers du XVIIIe siècle, un des premiers connus étant l'arbre botanique d'Augustin Augier (en) publié en 1801[2].
Le premier arbre phylogénétique qui s'inscrit dans une dimension temporelle et phylogénétique apparaît en 1809 dans les « Additions » à la fin de la Philosophie Zoologique (en) de Lamarck. Le naturaliste présente un « TABLEAU servant à montrer l'origine des différents animaux ». Son arbre de 1815 est encore plus explicite, s'intitulant « ordre présumé de la formation des animaux ». Mais les arbres de Lamarck sont encore tête en bas. Wallace et Darwin envisagent la notion de divergence sous forme d'arbre, respectivement suggéré en 1855[3] et dessiné en 1859[4], avec la tête en haut[5].
L'arbre phylogénétique de Darwin[modifier | modifier le code]



Darwin popularise le concept d'un arbre de la vie, dans son ouvrage De l'origine des espèces, publié le . Plus d'un siècle plus tard, les biologistes de l'évolution utilisent encore des diagrammes en forme d'arbre pour décrire l'évolution des espèces.
Voici un extrait de l'ouvrage L'Origine des espèces, publié le , dans lequel Darwin explique son point de vue sur l'arbre phylogénétique :
« Les affinités de tous les êtres de la même classe ont parfois été représentées sous la forme d'un grand arbre. Je crois que cette comparaison est très juste. Les rameaux verts et bourgeonnants peuvent représenter les espèces existantes; les branches produites les années précédentes peuvent représenter la longue succession des espèces éteintes. À chaque période de croissance tous les rameaux ont essayé de pousser de tous côtés, de surpasser et de tuer les rameaux et les branches environnantes, de la même manière que les espèces et les groupes d'espèces ont de tout temps vaincu d'autres espèces dans la grande bataille de la vie. Les plus grosses branches se sont divisées en grosses branches, et celles-ci en branches de moins en moins grosses, qui n'étaient autrefois, quand l'arbre était jeune, que des petits rameaux bourgeonnants ; et cette relation entre les anciens bourgeons et les plus récents au moyen de branches ramifiées pourrait bien représenter la classification de toutes les espèces éteintes et vivantes en groupes subordonnés à d'autres groupes. Sur les nombreux rameaux qui florissaient alors que l'arbre n'était qu'un arbuste, seulement deux ou trois, maintenant transformés en grosses branches, survivent encore et portent les autres branches; ainsi chez les espèces qui vivaient lors des anciennes périodes géologiques, très peu ont laissé des descendants vivants et modifiés. Dès la première croissance de l'arbre, de nombreuses branches ont péri et sont tombées ; et ces branches tombées, de taille variable, peuvent représenter ces ordres, ces familles et ces genres tout entiers, qui n'ont plus de représentants vivants, et que nous ne connaissons qu'à l'état de fossile. De la même façon que nous voyons ici et là une branche menue et isolée, surgissant d'une bifurcation inférieure, et qui, par chance a été favorisée et est encore vivante au sommet de l'arbre, nous voyons occasionnellement un animal tel que l'ornithorynque ou le lépidosirène, qui par de petits détails, connecte grâce à ses affinités deux grandes branches de la vie, et qui apparemment a été sauvé d'une compétition fatale par le fait qu'il vivait dans un habitat protégé. Tout comme les bourgeons produisent par croissance de nouveaux bourgeons, et que ceux-ci, s'ils sont vigoureux, forment des branches et surpassent de tous côtés les branches plus faibles, je crois qu'il en est de même pour le grand « arbre de la vie », qui remplit l'écorce terrestre avec ses branches mortes et brisées, et couvre sa surface avec ses belles ramifications toujours actives. »
Les arbres évolutifs de Haeckel[modifier | modifier le code]

Le naturaliste allemand Haeckel (1834-1919) et également le paléontologue français Albert Gaudry (1827-1908) sont, en 1866[8],[9], les premiers artisans de la représentation classique de la filiation des espèces sous la forme d'un arbre, l'arbre phylogénétique suivant le croquis de Darwin, unique illustration figurant dans De l'Origine des espèces (1859).
Tout au long de ses travaux scientifiques, Haeckel construisit différents types d'arbres généalogiques, les uns monophylétiques à racine unique, les autres polyphylétiques à racines multiples, qu'il appliquait à l'ensemble des organismes vivants, aux lignées végétales ou animales, aux groupes unicellulaires ou pluricellulaires, en suivant une graduation ordonnée des formes inférieures simples vers les formes supérieures complexes[10].
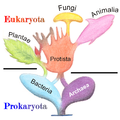
Influencé par les travaux de Darwin sur l'évolution, Haeckel fut le premier savant à dresser, en 1866[8], un arbre généalogique ou phylogénétique du monde vivant avec trois règnes, les Animaux (Animalia), les Plantes (Plantae) et les Protistes (Protista), descendant d'une seule et même origine. Le naturaliste allemand plaçait dans le règne des Protistes tous les êtres vivants ne répondant pas aisément aux critères définissant alors, au XIXe siècle, les organismes animaux et végétaux.
Dans ce règne, se trouvèrent ainsi réunis l'ensemble des algues et des champignons unicellulaires, les protozoaires, mais aussi les bactéries.
En 1874[11], Haeckel a proposé, sous le nom d'« arbre généalogique de l’homme », une phylogénie du règne animal construite d’après les données de l’anatomie et de l’embryologie comparées. Le savant allemand distinguait les Protozoaires (Protozoa), les Métazoaires invertébrés (Metazoa evertebrata), les Vertébrés (Vertebrata) et plaçait les Mammifères (Mammalia) au sommet de son arbre phylogénétique.
Dans la révision de son système naturel, en 1894[12], Haeckel suivait une quadripartition et rassemblait les organismes vivants en quatre règnes : I. Protophyta, II. Metaphyta, III. Protozoa, IV. Metazoa.
Dans une version finale en 1904[13], Haeckel réduisait son système à deux règnes : Protista pour les organismes ne formant pas de tissus et Histonia pour les organismes possédant des tissus.
L'arbre universel de Woese[modifier | modifier le code]

En 1977, des scientifiques dirigés par le microbiologiste américain Carl Woese (1928-2012) annoncent la découverte d'une nouvelle forme de vie qui bouleverse les fondements de la taxinomie biologique, alors basée sur la division dichotomique entre Procaryotes et Eucaryotes[16]. En procédant à une analyse phylogénétique des séquences de l'ARN ribosomique 16S constituant la petite sous-unité des ribosomes chez les procaryotes (par comparaison avec l'ARN ribosomique 18S constituant la petite sous-unité des ribosomes chez les eucaryotes), Woese et Fox (1977) ont mis en évidence l'existence de trois lignées anciennes, qui auraient toutes bifurqué séparément d'hypothétiques progénotes peu après le début de la vie. Ils proposent de reconnaître comme des « règnes primaires » ou urkingdoms : les archéobactéries Archaebacteria, les eubactéries Eubacteria et les urcaryotes représentés par le composant cytoplasmique des cellules des actuels eucaryotes Eucaryota[17].
Woese vulgarise, en 1981, un arbre phylogénétique représenté par trois grands troncs accolés, correspondant aux trois règnes primaires et dérivant à partir d'une souche commune, l'ancêtre universel (progénote). Il l'oppose à l'arbre conventionnel de la vie conçu par Margulis, à deux lignées ancestrales procaryote et eucaryote, la seconde descendant de la première par endosymbiose[18].
En 1990, Woese et ses collègues proposent de retenir un système naturel des organismes à trois domaines : les bactéries Bacteria, les archées Archaea et les eucaryotes Eucarya. Sur la base de cette approche, ils publient le premier « arbre universel de la vie », sous forme enracinée (dans la branche bactérienne) et montrant les trois domaines du monde vivant[15].
L'arbre de la vie aujourd'hui[modifier | modifier le code]
Ce modèle possède toujours un certain intérêt dans le cas des formes de vie eucaryotes, des plantes multicellulaires et des animaux, quoiqu'il soit probablement une représentation simplifiée de l'évolution. Les biologistes modernes reconnaissent maintenant que les procaryotes et les bactéries ont la capacité de transférer des informations génétiques à des organismes étrangers. La recombinaison, la perte, la duplication et la création génétique sont quelques-uns des processus grâce auxquels les gènes peuvent être transmis entre les différentes espèces de bactéries, ce qui entraîne une variabilité qui n'est pas due à un transfert vertical. L'arbre de la vie n'est pas un moyen valide pour modéliser la vie à ce niveau. Quant aux organismes multicellulaires (plantes et animaux), de nombreux biologistes considèrent que les transferts horizontaux de gènes (qu'ils soient dus à des hybridations ou à des recombinaisons résultant notamment de l'action de virus) sont un facteur de l'évolution bien plus important qu'on ne le pensait il y a quelques années encore[19]. L'arbre de la vie cachait une forêt[20].
Le Dr Ford Doolittle a notamment continué les recherches sur les arbres phylogénétiques. Selon Doolittle (1999)[21], de multiples transferts latéraux de gènes transforment l'arbre de la vie en une forme réticulée, ou « réseau » de la vie[22],[23].
Admettant la théorie de la fusion des génomes entre Bactéries et Archées (pour engendrer les Eucaryotes), d'autres biologistes comme Rivera et Lake (2004)[24] tendent à remplacer l'image de l'arbre par une forme circulaire, ou « anneau » de la vie[23],[25].
Des chercheurs en biologie de l'évolution comme Puigbò, Wolf et Koonin (2009-2013)[26],[27] considèrent que l'arbre de la vie représente une tendance statistique centrale de la « forêt phylogénétique » de la vie constituée d'une multitude d'arbres de gènes.
Le microbiologiste Raoult (2010)[28] préfère quant à lui l'hypothèse post-darwinienne du « rhizome » de la vie[29]. Avec son équipe de chercheurs, il met en lumière un possible « quatrième domaine de la vie » comprenant les grands virus nucléocytoplasmiques à ADN, comme Mimivirus, et émergeant, aux côtés des Bactéries, des Archées et des Eucaryotes, dans le rhizome de la vie[30].
Le botaniste Selosse (2011) vulgarise l'image du réseau fluvial et en particulier du delta pour représenter l'évolution par fusion. Il considère que les arbres évolutifs « classiques » demeurent valables mais ne reflètent qu’une partie de la réalité biologique, à savoir la seule évolution par divergence, et prennent trop peu en compte l’importance de l'évolution par fusion et de ses différents mécanismes (l'endosymbiose, les transferts de gènes, l'hybridation)[31].
Cependant, à côté de ces théories alternatives, certains biologistes comme le Pr Thomas Cavalier-Smith soutiennent qu'un arbre plus classique (sans fusion, sans réseau, sans anneau, sans rhizome…) permet de rendre compte de l'évolution du vivant et de l'apparition des grands embranchements bactériens de manière satisfaisante[32]. Selon cette dernière théorie, les eucaryotes sont un groupe-frère des archébactéries et tous deux sont des descendants des posibactéries (ou bactéries à Gram positif), elles-mêmes descendantes des négibactéries (ou bactéries à Gram négatif).
Le microbiologiste Forterre (2013)[33] considère les Virus comme des organismes à part entière, pouvant être introduits sous forme d'ensembles de lignées évolutives représentées par des lianes qui s’enroulent autour du tronc et des branches de l’arbre universel du vivant[34].
Des chercheurs en bio-informatique évolutive, Nasir et Caetano-Anollés (2015)[35], ont dressé un nouvel arbre de la vie où les Virus sont les descendants d'une lignée de protocellules distinctes du dernier ancêtre commun universel (DACU en français ou LUCA en anglais) et constituent une branche du vivant à part entière, aux côtés des Archées, des Bactéries et des Eucaryotes[36].
Définition et méthodes de construction[modifier | modifier le code]
Il existe plusieurs techniques de construction des arbres phylogénétiques, plus ou moins rapides et plus ou moins fiables.
Méthodes[modifier | modifier le code]
On peut être amené à chercher à optimiser plusieurs critères dans l'arbre : la distance, la parcimonie, ou la vraisemblance.
Pour les méthodes de distance, il s'agit tout d'abord de choisir le critère de distance entre les futures feuilles de l'arbre. Par exemple, si ces feuilles sont des séquences d'ADN, on peut choisir comme distance entre deux d'entre elles le nombre de nucléotides qui diffèrent. Pour déterminer cette valeur, on est amené à en effectuer un alignement. Puis on peut utiliser la méthode UPGMA ou celle du Neighbour joining pour en déduire l'arbre.
Les méthodes de parcimonie, aujourd'hui majoritairement représentées par la cladistique, sont plus utilisées pour les études morphologiques. En ce qui concerne les approches moléculaires, la parcimonie consiste à trouver l'arbre qui minimise le nombre de mutations, délétions, ou insertions ponctuelles pour passer d'une séquence à l'autre. Cette méthode recherche donc le réseau le plus économique en substitutions. Ainsi, si les longueurs des rameaux sont proportionnelles aux nombres de substitutions survenues, le réseau ayant la longueur totale la plus courte sera sélectionné. Ce principe sous-entend que les phénomènes de convergence évolutive et de réversibilité (retour d'un caractère à l'état ancestral) soient relativement rares. Ainsi, l'arbre présentant le moins d'étapes évolutives est celui qui minimise l'existence de ces deux phénomènes.
Cette méthode est divisée en trois étapes :
- A rechercher tous les arbres phylogénétiques possibles pour les différents taxons étudiés,
- B mesurer la longueur totale de chaque arbre,
- C sélectionner celui ou ceux qui présentent la longueur la plus petite.
Les arbres fournis par cette méthode sont non polarisés, cependant l'utilisation de groupe externe (espèces externes aux groupes étudiés) permet dans un deuxième temps de polariser l'arbre.
C'est une méthode très lente si l'on génère tous les arbres possibles pour en calculer la parcimonie.
Enfin, les méthodes de vraisemblance sont plus probabilistes. En se fondant sur le taux de substitution pour chaque élément de base (nucléotide pour des séquences d'ADN) au cours du temps, on estime la vraisemblance de la position et de la longueur des branches de l'arbre.
Racine[modifier | modifier le code]
Si l'on a obtenu un arbre non enraciné par une des méthodes ci-dessus, on peut tenter d'en trouver la racine par la méthode du groupe externe ou du point médian. Cette méthode (outgroup ou extragroupe) consiste à ajouter aux séquences traitées, avant le calcul de l'arbre, une très éloignée : le nœud-racine sera le père de cette séquence. Celle du point médian consiste à affecter à chaque nœud de l'arbre une séquence correspondant au consensus de ses fils, et choisir comme racine le nœud dont la séquence est la plus proche de la séquence consensus de toutes les feuilles.
Théorie des graphes[modifier | modifier le code]
De manière formelle, les arbres phylogénétiques peuvent être représentés et étudiés à l'aide d'objets mathématiques appelés des « graphes »[37]. En théorie des graphes, une généalogie et une phylogénie sont mathématiquement le même objet[38].
Par modélisation basée sur la théorie des graphes, les arbres de lignées, montrant des parentés, peuvent être englobés dans un ensemble plus large, les réseaux, représentant des organisations et des fonctionnements[39].
Arbre phylogénétique du vivant[modifier | modifier le code]

C'est un cas particulier d'arbre phylogénétique : celui des espèces vivantes.
Des débats existent entre les systématiciens pour déterminer les critères de classification les plus pertinents. Cette classification, dont une synthèse a paru en français sous le titre Classification phylogénétique du vivant est susceptible d'être encore grandement modifiée dans les années à venir, selon toute vraisemblance. La tentative de mise au point des connaissances actuelles en matière de classification mise en place par Guillaume Lecointre et Hervé Le Guyader n'est pas à considérer, comme ils le disent eux-mêmes, comme un document définitif. La 3e édition (2006)[40] de leur ouvrage présente déjà une évolution significative par rapport à la première parue en 2001.
L'arbre qui en résulte dans leur ouvrage se trouve à l'article suivant : Classification phylogénétique de Guillaume Lecointre et Hervé Le Guyader.
De plus, un arbre général du vivant cellulaire (sans les virus, donc) se trouve dans une série d'articles à partir de l'article intitulé Le vivant (classification phylogénétique). Il comporte une ramification développée jusqu'aux rangs immédiatement supérieurs aux genres, et a été actualisé. Les noms de taxons, sauf exception, y sont portés en latin, conformément aux conventions scientifiques internationales (et à la convention de nommage des taxons supérieurs au genre, dans cette Wikipédia). Il comporte les groupes éteints, qui augmentent parfois considérablement sa taille, y compris en largeur. C'est donc aussi pour une meilleure lisibilité qu'il a été découpé entre plusieurs articles, selon les taxons les plus « importants ».
Cet arbre a été représenté sous la forme d'un « buisson sphérique » dans le film documentaire Espèces d'espèces[41].
La représentation sous forme circulaire de l'arbre phylogénétique du vivant porte le nom de « graphique de Hillis »[42]. Créée par un groupe de recherche en bio-informatique, associé avec le biologiste Hillis[43], la figure incorporant 3000 espèces paraît en 2003[44].
Une méthodologie développée par Ciccarelli et al. (2006) permet de construire de manière automatisée des arbres phylogénétiques basés sur le génome[1],[45] : l'arbre phylogénétique du vivant, construit par une procédure enlevant tous les gènes supposés transmis horizontalement, est considéré par Dagan et Martin (2006) comme seulement « l’arbre de 1 % de la vie »[46].
Une application pour smartphones[47],[48] (disponible depuis fin 2016 sur l'App Store d'Apple[49] et depuis fin 2017 sur le Play Store d'Android[50]) intègre plusieurs millions d'espèces et permet de visualiser (avec zooms) les niveaux hiérarchiques et les relations entre espèces[51]. Elle offre des liens directs vers des images et des descriptions issues de Wikipédia.
Exemples d'arbres phylogénétiques[modifier | modifier le code]
(Les arbres qui illustrent cette section sont des exemples datés. Comme toute science, la systématique corrige ou affine continuellement ses résultats.)
Ainsi selon Lecointre et al., l'arbre de parenté et l'arbre à bulles (arbre évolutif commun du temps de la systématique éclectique, mêlant la généalogie, c'est-à-dire des relations de descendance et la phylogénie, de relations de parenté entre classes traditionnelles) sont considérés comme n'étant pas des « phylogénies » vraies[52]. Mais, sous forme circulaire, l'arbre de relations de parenté reste utilisé en 2017[53].
-
Arbre phylogénétique simplifié selon la classification phylogénétique, d’après Carl Woese.
-
Arbre phylogénétique indiquant également la taille des génomes.
-
Arbre phylogénétique montrant la relation entre les eucaryotes en rouge, les archées en vert et les bactéries en bleu.
-
Arbre de parenté des végétaux, d'après Stewart & Rothwell (2010)[54], Woese et al. (1990)[15], Lecointre & Le Guyader (2006)[40], López-García & Moreira (2008)[55].
-
Arbre à « bulles ».
Notes et références[modifier | modifier le code]
- (en) Cet article est partiellement ou en totalité issu de l’article de Wikipédia en anglais intitulé « Tree of life (science) » (voir la liste des auteurs).
Notes[modifier | modifier le code]
- L'arbre est constitué de trois troncs (le long desquels se disposent cinq tribus) et vingt branches (les classes), qui se subdivisent en cinquante-quatre rameaux (les ordres), pourvus de deux cent soixante-cinq feuilles (les familles)[6].
Références[modifier | modifier le code]
- (en) Francesca D. Ciccarelli, Tobias Doerks, Christian von Mering, Christopher J. Creevey, Berend Snel, Peer Bork, "Toward Automatic Reconstruction of a Highly Resolved Tree of Life", Science, Vol.311, No.5765, March 3, 2006, p.1283-1287. DOI 10.1126/science.1123061
- (en) P. F. Stevens, « Augustin Augier's "Arbre Botanique" (1801), a Remarkable Early Botanical Representation of the Natural System », Taxon, vol. 32, no 2, , p. 203-211.
- (en) Alfred Russel Wallace, « XVIII.—On the law which has regulated the introduction of new species », The Annals and Magazine of Natural History, London, Taylor & Francis, 2e série, vol. 16, no 93, , p. 184-196 (ISSN 0022-2933, DOI 10.1080/037454809495509). Référence Biodiversity Heritage Library : 2263944 .
- (en) Charles Darwin, On the Origin of Species by Means of Natural Selection, or the Preservation of Favoured Races in the Struggle for Life , John Murray, London, 1859.
- (en) James Fisher, Julian Huxley, The Doubleday pictorial library of nature : earth, plants, animals, Doubleday, , p. 163.
- D'après Jean Gayon, Le paradigme de la filiation, Paris, L'Harmattan, , 446 p. (ISBN 978-2-7384-3040-3, BNF 36689451), p. 39.
- (en) Darwin, C. (1872), pp. 170-171. The Origin of Species. Sixth Edition. The Modern Library, New York.
- (de) Ernst Haeckel, Generelle Morphologie der Organismen, Reimer, Berlin, 1866.
- Albert Gaudry, Considérations générales sur les animaux fossiles de Pikermi, F. Savy éditeur, Paris, 1866. [lire en ligne]
- (en) Benoît Dayrat, "The Roots of Phylogeny : How Did Haeckel Build His Trees?", Systematic Biology, Vol.52, No.4, August 1, 2003, p.515-527. DOI 10.1080/10635150390218277
- (de) Ernst Haeckel, Anthropogenie : oder, Entwickelungsgeschichte des Menschen, Engelmann, Leipzig, 1874.
- (de) Ernst Haeckel, Systematische Phylogenie der Protisten und Pflanzen, Vol.I, Georg Reimer, Berlin, 1894.
- (de) Ernst Haeckel, Die Lebenswunder : Gemeinverstdndliche Studien iiber Biologische Philosophie, Alfred Kröner Verlag, Stuttgart, 1904.
- Corinne Fortin, Guillaume Lecointre (dir.), Alain Bénéteau (dessins), Thomas Haessig (dessins) et Dominique Visset (dessins), Guide critique de l'évolution, Paris, Belin, , 571 p. (ISBN 978-2-7011-4797-0, OCLC 965978019).
- (en) Carl R. Woese, Otto Kandlert & Mark L. Wheelis, "Towards a natural system of organisms : Proposal for the domains Archaea, Bacteria, and Eucarya", Proc. Natl. Acad. Sci. USA, Vol.87, n° 12, 1-er juin 1990, p. 4576-4579, DOI 10.1073/pnas.87.12.4576
- (en) Richard D. Lyons, "Scientists Discover a Form of Life That Predates Higher Organisms", The New York Times, November 3, 1977, section A, p.1,20.
- (en) Carl R. Woese & George E. Fox, "Phylogenetic structure of the prokaryotic domain : The primary kingdoms", Proc. Natl. Acad. Sci. USA, Vol.74, No.11, November 1, 1977, p.5088-5090. DOI 10.1073/pnas.74.11.5088
- (en) Carl R. Woese, "Archaebacteria", Scientific American, Vol.244, No.6, June 1981, p.98-100,104,106,110,112,114,116,119-122. DOI 10.1038/scientificamerican0681-98
- (en) "Why Darwin was wrong about the tree of life", New Scientist, 21 January 2009 - https://www.newscientist.com/article/mg20126921.600
- Entretien avec Hervé Le Guyader (Propos recueillis par Marie-Neige Cordonnier), « L'arbre du vivant cachait une forêt», Pour la Science, Numéro spécial : Le nouveau monde des microbes, N°469, Novembre 2016, p.26-30.
- (en) W. Ford Doolittle (1999), "Phylogenetic Classification and the Universal Tree", Science 284 (5423) : 2124–2129, 25 June 1999. DOI 10.1126/science.284.5423.2124
- Christian de Duve, Singularités : Jalons sur les Chemins de la Vie, Odile Jacob, Paris, Avril 2005, p.205-206. (ISBN 2-7381-1629-9)
- Jacques van Helden, « Chapitre 9 : Ce que nous apprend l'analyse des génomes au sujet de l'évolution », sous la direction de Gérard Cobut, Comprendre l'évolution 150 ans après Darwin, coll. « Action ! », De Boeck, Bruxelles, 2009, p. 127-128. (ISBN 978-2-8041-0476-4).
- (en) Maria C. Rivera & James A. Lake (2004), "The ring of life provides evidence for a genome fusion origin of eukaryotes", Nature 431 (7005) : 152-155, 9 September 2004. DOI 10.1038/nature02848
- Christian de Duve, Singularités : Jalons sur les Chemins de la Vie, Odile Jacob, Paris, Avril 2005, p.204-205. (ISBN 2-7381-1629-9)
- (en) Pere Puigbò, Yuri I. Wolf & Eugene V. Koonin (2009), "Search for a ‘Tree of Life’ in the thicket of the phylogenetic forest", Journal of Biology 8 : 59, 13 July 2009. DOI 10.1186/jbiol159
- (en) Pere Puigbò, Yuri I. Wolf & Eugene V. Koonin (2013), "Seeing the Tree of Life behind the phylogenetic forest", BMC Biology 11 : 46, 15 April 2013. DOI 10.1186/1741-7007-11-46
- (en) Didier Raoult (2010), "The post-Darwinist rhizome of life", The Lancet 375 (9709) : 104-105, 9 January 2010. DOI 10.1016/S0140-6736(09)61958-9
- Didier Raoult, avec la collaboration de Véronique Dupont, Dépasser Darwin : L'évolution comme vous ne l'aviez jamais imaginée, Plon, Paris, p.148-153. (ISBN 978-2-259-21114-7)
- (en) Mickaël Boyer, Mohammed-Amine Madoui, Gregory Gimenez, Bernard La Scola, Didier Raoult, "Phylogenetic and Phyletic Studies of Informational Genes in Genomes Highlight Existence of a 4th Domain of Life Including Giant Viruses", PLoS One, Vol.5, No.12, December 2, 2010, p.e15530. DOI 10.1371/journal.pone.0015530
- Marc-André Selosse, « L'évolution par fusion », Pour la Science, N°400, Février 2011, p. 50-56.
- (en) Thomas Cavalier-Smith, « The neomuran origin of archaebacteria, the negibacterial root of the universal tree and bacterial megaclassification », International Journal of Systematic and Evolutionary Microbiology 52: 7–76 (2002)
- Patrick Forterre, « Les virus à nouveau sur le devant de la scène », Biologie Aujourd’hui, Vol.207, N°3, Société de biologie, 2013, p.153-168. DOI 10.1051/jbio/2013018
- Lionel Cavicchioli, « Microbiologie : Nos ancêtres les virus », Science & Vie, no 1227, , p. 88-91 (ISSN 2266-2324, résumé).
- (en) Arshan Nasir & Gustavo Caetano-Anollés (2015), « A phylogenomic data-driven exploration of viral origins and evolution », Science Advances 1 (8) : e1500527, 25 September 2015. DOI 10.1126/sciadv.1500527
- Román Ikonicoff, « Origine des virus : le nouveau scénario », Science & Vie, N°1179, Décembre 2015, p.75-77.
- Aubert 2017, section 2.3.2. « La terminologie phylétique », p. 51-54.
- Aubert 2017, « Arbre », p. 443.
- Entretien avec Éric Bapteste (Propos recueillis par Gérard Lambert), « Évolution : des réseaux plutôt que des arbres», Pour la Science, n°486, Avril 2018, p. 70-72.
- Guillaume Lecointre et Hervé Le Guyader, Classification phylogénétique du vivant, Paris, Belin, , 3e éd. (1re éd. 2001), 559 p., 1 vol. + 1 livret des arbres de la classification phylogénétique (ISBN 978-2-7011-4273-9, BNF 40140378).
- Buisson sphérique d'après le film documentaire Espèces d'espèces (2008).
- Aymeric Caron, « Les animalosceptiques, Partie I : la réponse de la génétique », dans Antispéciste : Réconcilier l'humain, l'animal, la nature, Don Quichotte, Paris, 2016, p.56. (ISBN 978-2-35949-498-3)
- (en) Richard Dawkins, The Greatest Show on Earth : The Evidence for Evolution, Simon & Schuster, New York, 2009, p.328. (ISBN 978-1-4165-9478-9)
- (en) Elizabeth Pennisi, "Modernizing the Tree of Life", Science, Vol.300, No.5626, June 13, 2003, p.1692-1697. DOI 10.1126/science.300.5626.1692
- (en) Russ Hodge, "A new tree of life", Science in School, No.2, Summer 2006, p.17-19. (ISSN 1818-0353)
- (en) Tal Dagan & William Martin, "The tree of one percent", Genome Biology, Vol.7, No.118, November 1, 2006. DOI 10.1186/gb-2006-7-10-118
- « Lifemap » (consulté le ).
- (en) Damien M. de Vienne, « Lifemap: Exploring the Entire Tree of Life », PLoS Biology, vol. 14, no 12, , article no e2001624 (DOI 10.1371/journal.pbio.2001624).
- « Une plongée vertigineuse dans la diversité du monde vivant », sur CNRS (consulté le ).
- « L’arbre du vivant disponible sur tablettes et smartphones », sur CNRS (consulté le ).
- Denis Faure (dir.), Dominique Joly (dir.) et Sylvie Salamitou (dir.), 101 secrets de l'ADN, Paris, CNRS Éditions, , 357 p. (ISBN 978-2-271-12323-7, SUDOC 240440471, présentation en ligne), chap. 1 (« Exploration haut débit du vivant : 1 Explorer et représenter la totalité de l'arbre du vivant »), p. 28-30.
- Corinne Fortin, Gérard Guillot, Guillaume Lecointre (dir.) et Marie-Laure Le Louarn-Bonnet, Guide critique de l'évolution : sous la direction de Guillaume Lecointre, Paris, Éditions Belin / Humensis, (réimpr. 2015), 1re éd., 571 p., xvi pl. [détail de l’édition] (ISBN 978-2-7011-4797-0, BNF 42116796), Partie I : Notions clés, difficultés classiques et débats récurrents, chap. 4 (« Les difficultés de compréhension de la théorie de l'évolution »), section 1.4. (« L'évolution = un arbre qui établit les relations d'apparentement entre tous les êtres vivants »), p. 65-67 & section 1.5. (« L'évolution = la marche, souvent linéaire, vers le progrès organique, culturel, social et même technique »), p. 67-69.
- Jean-François Buoncristiani & Pascal Neige, 101 merveilles de l'évolution qu'il faut avoir vues dans sa vie, Dunod, Paris, 2017, p.12.
- (en) Wilson Nichols Stewart et Gar W. Rothwell, Paleobotany and the Evolution of Plants, Cambridge, Cambridge University Press, (réimpr. 2011), 2e éd. (1re éd. 1993), xii + 521 (ISBN 978-0-521-12608-3).
- (en) Purificación López-García et David Moreira, « Tracking microbial biodiversity through molecular and genomic ecology », Research in Microbiology, vol. 159, no 1, , p. 67–73 (DOI 10.1016/j.resmic.2007.11.019)
Voir aussi[modifier | modifier le code]
Bibliographie[modifier | modifier le code]
![]() : document utilisé comme source pour la rédaction de cet article.
: document utilisé comme source pour la rédaction de cet article.
- Damien Aubert, Classer le vivant : Les perspectives de la systématique évolutionniste moderne, Paris, Ellipses, , 496 p. [détail de l’édition] (ISBN 978-2-340-01773-3, BNF 45296689)

- (en) Pietsch, T.W., Trees of life : a visual history of evolution, Baltimore, MD, USA, Johns Hopkins University Press, , xi, 358 (lire en ligne
 )
) - Éric Tannier, Bastien Boussau et Vincent Daubin, « Quand les branches de l'arbre du vivant s'entremêlent », Pour la science, no 506, , p. 56-65
Articles connexes[modifier | modifier le code]
- Alignement de séquences
- Bio-informatique
- Classification phylogénétique
- Le vivant (classification phylogénétique)
- Phylogénie
- Scala naturæ
Liens externes[modifier | modifier le code]
- (fr) [audio] "Vivant, la fin d’un règne ?", La Méthode Scientifique, France Culture, 25 mars 2019
- (fr) « Fabriquer un arbre phylogénétique »(Archive.org • Wikiwix • Archive.is • Google • Que faire ?)
- (fr)Construire un arbre phylogénétique et l'interpréter
- (en) Tree of Life Web Project
- (en) NCBI Taxonomy
- (en) Time tree, the timescale of life
- (en) Musée de paléontologie de l'Université de Californie, Berkeley
- (en) « Mikko's Phylogeny Archive »
- (en) Palaeos.com et (en) « Palaeos.org »(Archive.org • Wikiwix • Archive.is • Google • Que faire ?)
- (en) Angiosperm Phylogeny Website
- (en) Man and Mollusc


![Arbre botanique d'Augustin Augier publié en 1801[a].](http://upload.wikimedia.org/wikipedia/commons/thumb/1/14/Augier_tree_of_life.jpg/84px-Augier_tree_of_life.jpg)






![Arbre de parenté des végétaux, d'après Stewart & Rothwell (2010)[54], Woese et al. (1990)[15], Lecointre & Le Guyader (2006)[40], López-García & Moreira (2008)[55].](http://upload.wikimedia.org/wikipedia/commons/thumb/8/8a/Phylog%C3%A9nie_v%C3%A9g%C3%A9tale.png/63px-Phylog%C3%A9nie_v%C3%A9g%C3%A9tale.png)